Inhaalproject3
Introductie
Infectieziekten zijn wereldwijd een belangrijke oorzaak van morbiditeit en mortaliteit. Dit wordt verder verergerd door antimicrobiële resistentie (AMR). AMR is het vermogen van micro-organismen om antimicrobiële behandelingen te weerstaan. Hoewel we over een zeer groot aantal antimicrobiële middelen beschikken, wordt voor elk van deze reagentia beschreven dat microben resistentie vertonen. Bacteriën die resistentie vertonen tegen ten minste drie verschillende klassen antimicrobiële stoffen worden gedefinieerd als multiresistent (MDR) en zijn een groot probleem in ziekenhuizen. Om AMR te begrijpen moeten we kennis vergaren over de moleculaire mechanisme die een bacterie gebruikt om resistent te worden en welke genen hierbij betrokken zijn (AMR genotypes). Verder is van belang om te weten tegen welke antibiotica (drug classes) de bacterien resistent zijn en in welke mate.
Om AMR te bestuderen zijn er speciale databanken:
(1) De NCBI pathogen databank gebruikt genoom sequenties van bacterien om AMR genen te detecteren. Deze bacteriele genoom sequenties worden bijvoorbeeld verkregen uit patienten in Nederlandse ziekenhuizen (of andere plekken in de wereld). Binnen deze databank kan je met behulp van de isolate browser lijsten verkijgen met (Nederlandse) bacterien en de aanwezigheid van AMR genen (AMR genotypes).
(2) De CARD (The Comprehensive Antibiotic Resistance Database) databank. In deze databank kan algemene informatie worden opgezocht over AMR genen, DNA/protein sequenties, geassocieerde resistentie mechanisms en antibiotica drugs classes. Verder is er onder andere een BLAST tools aanwezig om te zoeken naar AMR genen binnen andere bacterie soorten
Opdracht3
In deze opdracht gaan jullie je verdiepen in AMR genen in bepaalde bacterie soorten in Nederland:
Hoe beinvloedt antibiotica de expressie van AMR genen in bacteria?
Opdracht3
In deze opdracht gaan jullie je verdiepen in het mexX gen. Dit gen speelt een rol in antimicrobiele resistentie in Pseudomonas aeruginosa:
Hoe beinvloedt antibiotica de expressie van het mexX gen in Pseudomonas aeruginosa?
De opdracht:
- Verkrijg het GFF3 bestand van Pseudomonas aeruginosa (zie les2 van de reader)
- Selecteer de regels van het GFF3 bestand die het woord “mRNA” bevatten met behulp van de bash
grepcommand en selecteer alleen de eerste 5 kolommen van dit bestand met behulp van de bashcutcommand
- Voeg de volgende kolomnamen toe aan het bestand (op de eerste regel): contig source type start end
(Dit kan via bash, Excel of Notepad / kladblok)
- Laad het bestand in JASP en bereken de mediaan van de genlengtes (= end - start)
- Laat ook een distributie plot en een boxplot zien van de genlengtes
Laat zien in het rapport welke bash commands / code je gebruikt hebt om de eerste twee stappen uit te voeren.
Als de de eerste 3 stappen niet gelukt zijn ga verder met bestand PA_gff3_out.txt die aanwezig is in server folder /home/data/das3v22/project_2024/inhaalproject
- Wat is het “resistance mechanism” van het MexX gen?
- Gebruik de CARD databank om een antwoord te verkrijgen op deze vraag
- Is er een verband tussen de hoeveelheid genexpressie van het mexX gen en de “growth inhibition zone”. De “growth inhibition zone” wordt bepaald met een disk diffusie assay (zie figuur hieronder voor uitleg)
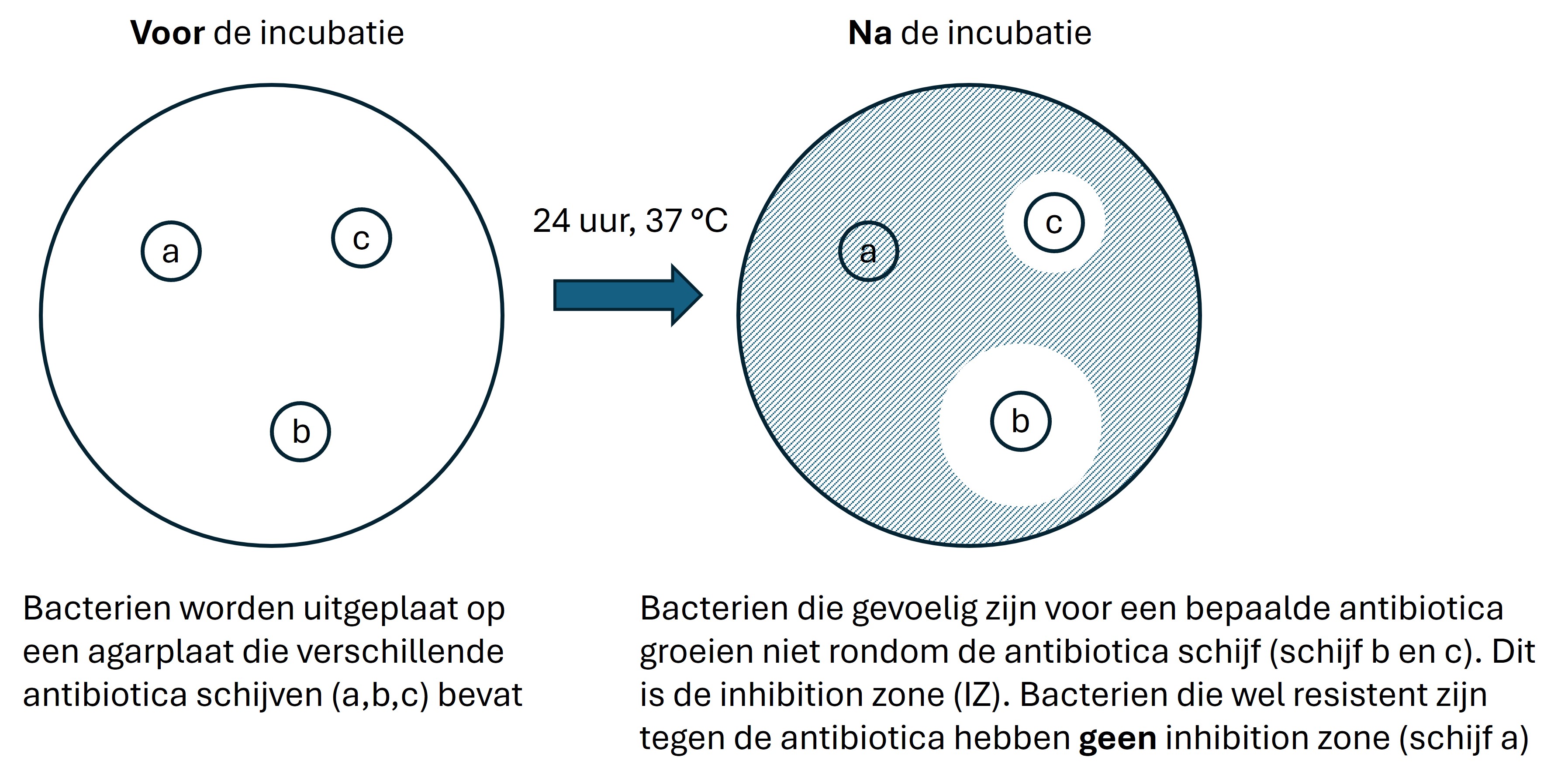
Figure 102: Experimentele opzet antibiotica en AMR genexpressie
Van 10 resistente bacterie isolaten is de (genormaliseerde) genexpressie bepaald van het mexX gen door middel van sequencing. Ook is de groeiremming van deze isolaten bepaald onder invloed van een antibioticum. De data staat in /home/data/das3v22/project_2024/inhaalproject/. Ga ervan uit dat de data normaal verdeeld is.
Analyseer de data in JASP:
+ Voer een correlatie analyse uit op de dataset in JASP
+ Voer een regressie analyse uit op de dataset in JASP
+ Voorspel met behulp van de regressielijn de inhibition zone als de genexpressie een waarde heeft van: 30
(Laat zien hoe je aan het antwoord komt!)
LET OP: Het is de bedoeling dat je je kennis van Blok A mobiliseert om de onderzoeksvraag te beantwoorden. Er is dus geen eenduidig antwoord op de onderzoeksvraag. Dit hangt af van de strategie die je gaat gebruiken (zie ook hieronder bij het werkplan).
- Verkennen en verdiepen:
- Zoek algemene (moleculaire) informatie op over antimicrobiele resistentie mechanismen
Schrijf een korte inleiding van ongeveer 10 regels (inclusief bronverwijzing naar research papers en databanken. Zonder bronvermelding geen punten!!)
- Onderzoeksvraag:
- Stel een hypothese op voor de onderzoeksvraag.
- Experiment (In silico)
- Beantwoord vraag1 t/m 3
- Data management
- Pas data management toe zoals beschreven in de project introductie
- Welke data bestanden ga je verkrijgen en hoe ga ik deze bestanden noemen
- In welke folder op de server ga ik deze bestanden bewaren?
- Kan de docent aan de hand van mijn beschrijvingen dezelfde data verkrijgen en dezelfde analyse uitvoeren (en tot dezelfde conclusie komen)
- Pas data management toe zoals beschreven in de project introductie
- Data analyse + Conclusie
- Wat is het antwoord op de onderzoeksvraag?
- Onderbouw je conclusie met de uitkomst van de data analyse van vraag3
- Wat is het antwoord op de onderzoeksvraag?